Hallo Craterelle!
Wir müssen uns da Stück für Stück vorkämpfen. Normalerweise wahrscheinlich eher ein Abend-Thema in trauter Runde mit einem Kasten Bier unter oder Weingläser auf dem Tisch.
Also ich bin ja auch nur Nutzer, und kriege lediglich so am Rande einiges mit, wovon ich aber auch gar nicht alles verstehe.
Fangen wir mal an, was man so braucht.
Also zum 1. einen Finder.
Das hört sich nach dem leichten Part des ganzen an, ist aber für 2., den Bestimmer eigentlich nur dann von Interesse, wenn er sich ordentlich am Standort umguckt und das Wichtige dokumentiert, sich also das Substrat oder die Begleitbäume und Pflanzen oder die Lage am Substrat, Vermorschungsgrad usw. ordentlich anschaut und als Info weitergibt. Den Wert von Infos kennen wir ja vom Forum.
Nach erfolgter Dokumentation und vielleicht sogar gelungener Artbestimmung brauchen wir 3. jmdn., der eine Kultur anlegt, damit wirklich später auch genau eben dieser Organismus die Sequenz hergibt, die wir wollen. Dazu gibt es verschiedene Verfahren, vielleicht sagt da Florian was dazu.
Irgendwann ist die Kultur so weit, dass man ihr tatsächlich so eine schöne lange Eiweißkette entlocken kann. Wie das genau geschieht, kann ich mir noch nicht vorstellen, da bekomme ich aber vielleicht mal einen kleinen Einblick, wenn es passt.
Aus dieser Kette, bestehend aus einer Aneinanderreihung von 4 verschiedenen Basen (gekürzelt C,G,T und A) sucht sich ein weiterer Wissender genau den Abschnitt heraus, der z.B. bei Weichbecherchen, der veränderliche ist, also der, aus dem man was lesen kann, was Unterschiede betrifft.
Um so gleicher jetzt der veränderliche Abschnitt ist, desto näher sind demzufolge die untersuchten Arten verwandt.
Um das zu managen, braucht man aber jetzt jmdn, der sich mit dem richtigen Auslesen des Sequenzabschnittes auskennt, auch die Programme dazu hat, das ganze vor- und rückwärts zu lesen und richtig interpretieren kann usw.
Und dann ist es natürlich gut, wenn derjenige, die Information über die Nähe der Verwandtschaft der untersuchten Arten der Übersichtlichkeit halber in so Genbäumchen bastelt. Das wirst du im Netz finden oder ich kann beim nächsten Mal sowas einstellen. Aufpassen muss man halt bei so einer Gemeinschaftsproduktion, dass sich keiner übergangen fühlt. Also ich werde da jetzt kein aktuelles Genbäumchen zeigen, dass die Verwandtschaftsverhältnisse der "holzbewohnenden, verstecktwachsenden Weichbecherchen im Sommer 2016" präsentiert oder so ähnlich.
Manchmal sind Sequenzen in der Genbank hinterlegt, auf die man Zugriff hat (da ist aber auch viel Bestimmungsmüll dabei).
Andere behalten ihre Erkenntnisse logischerweise erst mal für sich, weil sie die irgendwann selbst publizieren wollen.
Das ist alles sehr vereinfacht erzählt. Da kommt noch einiges an Problemen dazu, z.B., dass mitten in den Gensequenzabschnitten auch mal Stücke sind, die man rausschneiden muss oder auch verschiedene Untersuchungsmethoden, die natürlich je umfangreicher sie sind auch immer teurer werden.
Ich las mal eine Anzeige eines spanischen Anbieters, der bot die Gensequenz (war es ITS?) für um die 35 Euronen an.
Schätze, da gibt es aber erstens Qualitätsunterschiede, und dann wird man vielleicht auch Mengenrabatt bekommen. Inzwischen kann sich das auch geändert haben, schließlich ist das Thema momentan ein großes Thema.
Das soll es erst mal für ´s erste sein. In meinem Geschriebenen sind sicherlich einige Dinge unfachmännisch oder suboptimal dargestellt, aber dann fühlt sich vielleicht der nächste bemüßigt, was dazu zu schreiben oder zu verbessern.
Ich hänge später mal so einen Sequenzabschnitt mit an oder auch ein Bäumchen.
VG Ingo W
[hr]
Hallo!
Hier also mal ein unscharf gemachtes Sequenzbäumchen (damit ich keinen Ärger kriege), aber das Prinzip wird sicherlich klar.
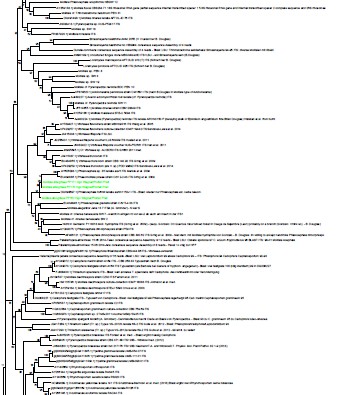
Mittig sind 3 grüne Einträge, das ist eine häufige Mollisia-Art, für die es aber bisher keinen guten Namen gibt.
In dem Zusammenhang hat sich aber eine hinterlegte Sequenz einer Nebenfruchtform als höchstwahrscheinlich zugehörig erwiesen (die Gabel drüber, zwischendrin der "Zweig" ist unklar.).
Da diese NFF einen publizierten Namen hat, wäre also das Problem der Mollisia-Namenslosigkeit theoretisch gelöst.
VG Ingo W
[hr]
Und so muss man sich den in Buchstaben übersetzten relevanten Sequenzabschnitt vorstellen, den es auszuwerten gilt.
Wie gesagt, 4 unterschiedliche Basen in Buchstabenform:
AACCTGCGGAAGGATCATTAACAAACCTCAGGCGCTCGCGCCCACAGGTAACCCTTGAATAAACTAC
CTTTGTTGCTTTGGCGGGCCGCCTTAGACTCTATAGCGAGGAGAAATTACTACCGTAGAACCTATCGGAACCGCCCGTGGACT
TGAGGGCTGCAGCCAAAGCCGCAACCCCAACATCAAGCCTAAGCTTGGTCATTTGTGTTGTTCTTACGACGCTCGACTCCGGC
CAGCGGCTTCGGCTGCTGCGCGCCCGCCAGAGGACCACAACTCTTGTTTTTAGTGATGTCTGAGTACTATATAATAGTTAAAAC
TTTCAACAACGGATCTCTTGGTTCTGGCATCGATGAAGAACGCAGCGAAATGCGATAAGTAATGTGAATTGCAGAATTCAGTGAA
TCATCGAATCTTTGAACGCACATTGCGCCCTTTGGTATTCCGAAGGGCATGCCTGTTCGAGCGTCATTATAACCACTCAAGCCTTC
GCTTGGTATTGGGGCTCGCGGTCGCGCGGCCCCTAAAATCAGTGGCGGTGCCGGCTGGCTCTACGCGTAGTAATACTCCTCGCGTCT
GGGTCCGGTCGGTTGCCTGCCAGCAA
VG Ingo W


